Sageでグラフを再現してみよう:データ解析のための統計モデリング入門第7章
この企画は、雑誌や教科書にでているグラフをSageで再現し、 グラフの意味を理解すると共にSageの使い方をマスターすることを目的としています。
前回に続き、データ解析のための統計モデリング入門 (以下、久保本と書きます) の第7章の例題をSageを使って再現してみます。
久保本もようやくテーマの個体差が大きい場合の例題に入りました。今回のグラフは図7.10です。以下に久保本から引用します。

数式処理システムSageのノートブックは、計算結果を表示するだけではなく、実際に動かすことができるのが大きな特徴です。 この機会にSageを分析に活用してみてはいかがでしょう。
前準備
最初に必要なライブラリーやパッケージをロードしておきます。
|
|
個体差の大きなデータ
7章の例題は、個体$x_i$で観測された以下のデータを含みます。
- 調査種子数$N_i = 8$
- 生存種子数$y_i$
- 葉数$x_i$
- 個体識別番号id
データの特徴と可視化
いつもの通りデータを読み込み、その内容、統計情報をチェックします。
N y x id 0 8 0 2 1 1 8 1 2 2 2 8 2 2 3 3 8 4 2 4 4 8 1 2 5 N y x id 0 8 0 2 1 1 8 1 2 2 2 8 2 2 3 3 8 4 2 4 4 8 1 2 5 |
N y x id count 100 100.000000 100.000000 100.000000 mean 8 3.810000 4.000000 50.500000 std 0 3.070534 1.421338 29.011492 min 8 0.000000 2.000000 1.000000 25% 8 1.000000 3.000000 25.750000 50% 8 3.000000 4.000000 50.500000 75% 8 7.000000 5.000000 75.250000 max 8 8.000000 6.000000 100.000000 N y x id count 100 100.000000 100.000000 100.000000 mean 8 3.810000 4.000000 50.500000 std 0 3.070534 1.421338 29.011492 min 8 0.000000 2.000000 1.000000 25% 8 1.000000 3.000000 25.750000 50% 8 3.000000 4.000000 50.500000 75% 8 7.000000 5.000000 75.250000 max 8 8.000000 6.000000 100.000000 |
同じ点に重なるデータの可視化
プロットデータを見ると、とても100個のデータがあるようには見えません。 これは、種子数・葉数が整数で同じ点に複数のデータが重なっているからです。
<ggplot: (8786367296557)> <ggplot: (8786367296557)> |
Saving 11.0 x 8.0 in image. Saving 11.0 x 8.0 in image. |
残念ながら、python版のggplotでは同じ点を重ならないようにするjitter機能が使えないため、 Rのggplot2を使ってプロットしてみました。
これで、データのばらつきが正しく把握できました。
|
|
|
|
GLMを使った分析
このデータを6章と同じようにGLMで分析してみます。 予測値は直線となっており、6章のようなロジスティック曲線にはなっていません。
Call:
glm(formula = cbind(y, N - y) ~ x, family = binomial, data = d)
Deviance Residuals:
Min 1Q Median 3Q Max
-4.4736 -2.1182 -0.5505 2.3097 4.0966
Coefficients:
Estimate Std. Error z value Pr(>|z|)
(Intercept) -2.1487 0.2372 -9.057 <2e-16 ***
x 0.5104 0.0556 9.179 <2e-16 ***
---
Signif. codes: 0 ‘***’ 0.001 ‘**’ 0.01 ‘*’ 0.05 ‘.’ 0.1 ‘ ’ 1
(Dispersion parameter for binomial family taken to be 1)
Null deviance: 607.42 on 99 degrees of freedom
Residual deviance: 513.84 on 98 degrees of freedom
AIC: 649.61
Number of Fisher Scoring iterations: 4
Call:
glm(formula = cbind(y, N - y) ~ x, family = binomial, data = d)
Deviance Residuals:
Min 1Q Median 3Q Max
-4.4736 -2.1182 -0.5505 2.3097 4.0966
Coefficients:
Estimate Std. Error z value Pr(>|z|)
(Intercept) -2.1487 0.2372 -9.057 <2e-16 ***
x 0.5104 0.0556 9.179 <2e-16 ***
---
Signif. codes: 0 ‘***’ 0.001 ‘**’ 0.01 ‘*’ 0.05 ‘.’ 0.1 ‘ ’ 1
(Dispersion parameter for binomial family taken to be 1)
Null deviance: 607.42 on 99 degrees of freedom
Residual deviance: 513.84 on 98 degrees of freedom
AIC: 649.61
Number of Fisher Scoring iterations: 4
|
|
|
久保本に従い、$x_i = 4$のデータを抽出し、そのヒストグラムとGLMから推定された 二項分布を表示してみましょう。
以下の様にPandasの抽出機能を使ってx=4のデータを取り出し、頻度を求めます。 これにロジスティック_logisticと二項分布_pの2つの関数を定義します。
y 0 3 1 1 2 4 3 2 4 1 5 1 6 2 7 3 8 3 dtype: int64 y 0 3 1 1 2 4 3 2 4 1 5 1 6 2 7 3 8 3 dtype: int64 |
|
|
|
|
GLMで求まったモデルを使って、x=4でのqの値をロジスティック関数から求めます。
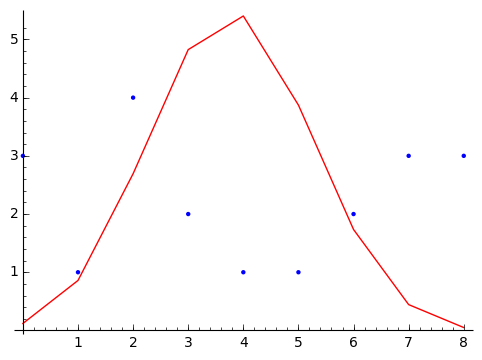
x=4での種子数分布(青点)と推定された二項分布(_p関数の値)にデータ数(tbl4.sum()=20)を掛けた値が、 推定された種子数になります。
このグラフからは、推定された種子数は、観測された種子数を説明しているように思えません。 久保本の説明では、$x_i = 4$の生存種子数の平均と分散を求めてみると、平均4.05に対して、 分散は8.37と大きく、二項分布の分散$N p (1-p)$から期待される値$8\times0.5\times(1-0.5)=2$と 比べて4倍ほど大きな値となっています。久保本ではこの状態を「ばらつきが大きすぎる」過分散と呼んでいます。
0.472527695655406 0.472527695655406 |
|
4.05 8.36578947368 4.05 8.36578947368 |
1.99396217995198 1.99396217995198 |
一般化線形混合分布(GLMM)を使った分析
個体差を考慮した分析手法として一般化線形混合分布(GLMM)が出てきます。
ここでは、個体$i$の個体差を$r_i$とし、以下の様なリンク関数を定義します。 $$ logit(q_i) = \beta_1 + \beta_2 x_i + r_i $$
ここで$r_i$をどのような分布にするかですが、久保本では平均0,分散$s$の正規分布と しています。(統計モデルとして便利だからと理由です)
glmmMLを使った分析では、個体毎に異なる独立パラメータをclusterオプションで指定します。 ここでは、idが個体を識別する指標として使われています。
[1] "glmmML" "jsonlite" "ggplot2" "stats" "graphics" "grDevices" "utils" "datasets" [9] "methods" "base" [1] "glmmML" "jsonlite" "ggplot2" "stats" "graphics" "grDevices" "utils" "datasets" [9] "methods" "base" |
Call: glmmML(formula = cbind(y, N - y) ~ x, family = binomial, data =
d, cluster = id)
coef se(coef) z Pr(>|z|)
(Intercept) -4.190 0.8777 -4.774 1.81e-06
x 1.005 0.2075 4.843 1.28e-06
Scale parameter in mixing distribution: 2.408 gaussian
Std. Error: 0.2202
LR p-value for H_0: sigma = 0: 2.136e-55
Residual deviance: 269.4 on 97 degrees of freedom AIC: 275.4
Call: glmmML(formula = cbind(y, N - y) ~ x, family = binomial, data = d, cluster = id)
coef se(coef) z Pr(>|z|)
(Intercept) -4.190 0.8777 -4.774 1.81e-06
x 1.005 0.2075 4.843 1.28e-06
Scale parameter in mixing distribution: 2.408 gaussian
Std. Error: 0.2202
LR p-value for H_0: sigma = 0: 2.136e-55
Residual deviance: 269.4 on 97 degrees of freedom AIC: 275.4
|
結果の可視化
GLMとの違いは、分析結果から予測される二項分布を見ると明らかです。 GLMのようなfitted.valuesがGLMMにはないので、分析結果の二項分布をmyfuncで定義して、 stat_function使ってプロットしてみました。
きれいに二項分布が表示されました。(これが図7.10の(A))
|
|
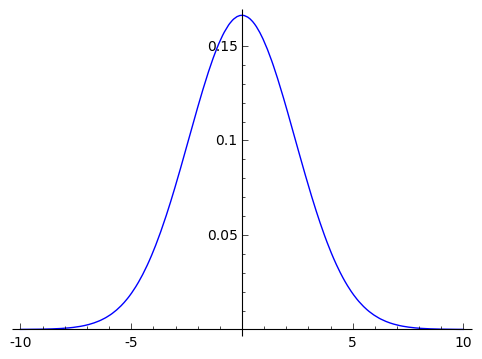
$r_i$の分布
もう一つGLMMから求められた$r_i$の正規分布をプロットすると以下の様になります。 -10, 10ではほぼ0になっています。
|
GLMMから求められた尤度
個体毎の尤度$L_i$は、以下の様に$r_i$を積分して求めることができます。 $$ L_i = \int_{-\infty}^{\infty} p(y_i | \beta_1, \beta_2, r_i) p(r_i | s) dr_i $$
GLMMの結果からqを求める関数_qを定義し、上記の積分をSageの数値積分を使って計算する関数_Liを以下の様に 作りました。rの積分範囲は、sの分布から-10から10としました。
チェックのために、久保本図7.8にあるx=4, r={-2.20, -0.60, 1.00, 2.60}のqの値と、 y={0, 4, 7}の尤度$L_i$を出力してみました。
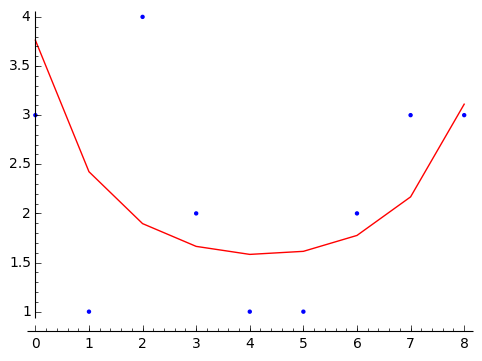
最後に、Liに20(個体数)を掛けた分布をx=4のヒストグラムに重ね合わせてみました。 きれいに、図7.10(B)の通り、生存種子数を表現できているのが分かります。
このような積分を含む処理でも数式処理システムSageを使えば簡単に分析できるのが、 ご理解頂けたと思います。
|
|
(0.0854891394348065, 0.316479106263684, 0.696354929823834, 0.919086532784535) (0.0854891394348065, 0.316479106263684, 0.696354929823834, 0.919086532784535) |
(0.18814448426796998, 0.07913801041038665, 0.10840844640974827) (0.18814448426796998, 0.07913801041038665, 0.10840844640974827) |
|
|
|



